前言
遗传算法的编码方法各种各样,但二进制串编码方式是最经典的一种,那么它的编码和解码该如何进行呢?或许本博客能给你一个具有参考价值的答案。
编码
经典遗传算法中使用“染色体”来代指个体,它由二进制串组成,如下图所示:

它的每一维称为一个基因,取值为0或1。
下面用一个具体的优化问题来解释个体(染色体)的编码和解码:
m
a
x
m
i
z
e
f
(
x
)
=
−
x
2
+
10
cos
(
2
π
x
)
+
30
,
−
5
≤
x
≤
5
maxmize \ f(x)\ =\ -x^2+10\cos{(2\pi x)}+30,\ -5\le x \le 5
maxmize f(x) = −x2+10cos(2πx)+30, −5≤x≤5
对于上述待优化函数,我们的编码应该设置多长的二进制串呢?
我们首先明确,编码长度取决于自变量的范围(更准确点应该是决策变量的范围)和搜索精度,所以围绕它们来考虑如何编码。
在本例,我们假设精度是0.01,记清楚了,是 0.01。
首先,我们可以确定自变量的范围(更准确点应该是决策变量的范围)是5-(-5)= 10.
另外,我们需要的精度是0.01,也就是说我们要能用我们的编码把自变量范围10以10.00表示,但二进制串只能表示整数没法表示小数(其实可以表示小数的,但我们不讨论这种情况),所以我们换个思路,我们用1000来表示10.00,但请注意,二进制串转化为十进制时不能刚好得到1000,而是得到
2
n
2^n
2n,所以我们得找到一个最大值大于1000的二进制串。
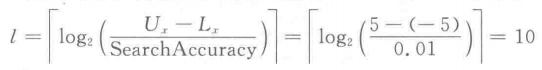
根据上图,我们发现可以用长度为10的二进制串来“容纳”上述的1000,为什么我用“容纳”来表述呢?因为长度为10的二进制串可以表示
0
∼
(
2
10
−
1
)
0 \thicksim (2^{10}-1)
0∼(210−1),也就是
0
∼
1023
0 \thicksim 1023
0∼1023,有
1023
>
1000
1023>1000
1023>1000;而
0
∼
(
2
9
−
1
)
0 \thicksim (2^{9}-1)
0∼(29−1)是
0
∼
511
0 \thicksim 511
0∼511, 有
511
<
1000
511<1000
511<1000 ,所以用1023来表示10.00,编码时二进制串长度为10,而不是9。
由上图公式,我们把初始群体的每个个体用一个长度为10的二进制串来表示,记为:
A
10
A
9
A
8
.
.
.
A
3
A
2
A
1
A_{10}A_{9}A_{8}...A_{3}A_{2}A_{1}
A10A9A8...A3A2A1
解码
在上一小节我们用1023来表示10.00,那解码的时候表示1023的二进制串如何表示回10.00呢?
想想,我们编码时把10.00放大成1023,那么解码时缩小1023倍就行了!
这样,我们解码的时候做如下处理:
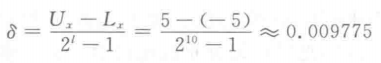
10.00 /1023 ≈ 0.009775,我们把解码出来的十进制数都乘以0.009775,就得到了最终结果。
于是有:

其中
L
x
=
−
5
L_x = -5
Lx=−5。
x
x
x 就是解码所得十进制数。
补充
这里要稍微注意下,实际搜索精度与期望搜索精度之间是存在误差的:
我们本想用1000来表示10.00的,但由于二进制串只能表示
2
n
2^n
2n,所以只好用1023来表示10.00,之后在

这里没法除尽产生了误差。
参考资料:
《人工智能及其应用第五版》- 蔡自兴